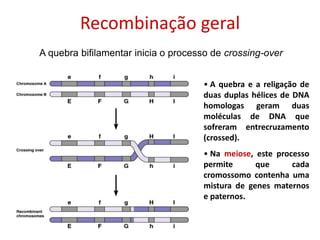
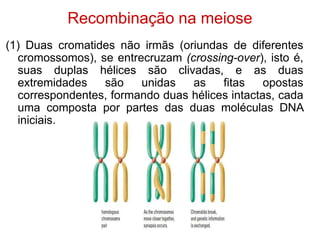
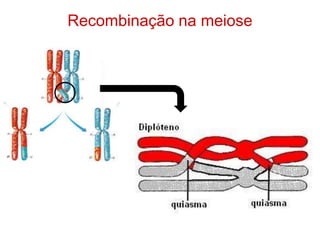
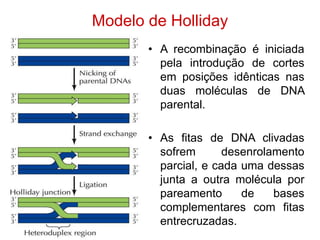
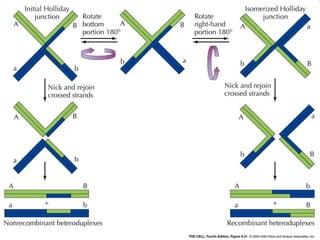
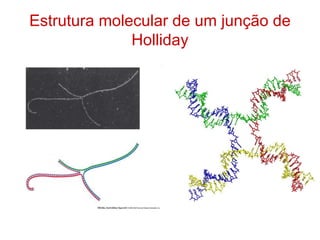
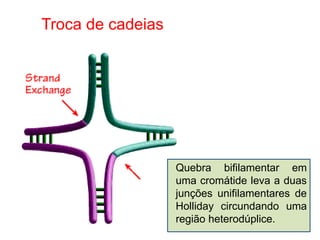
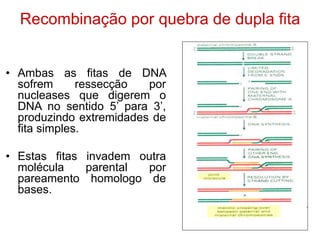
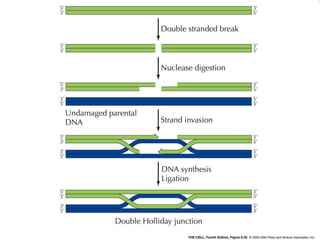
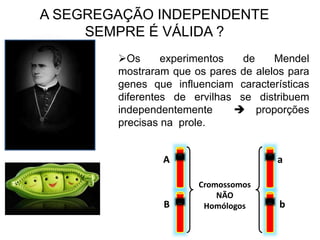
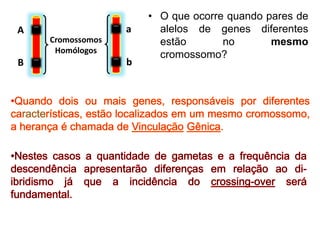
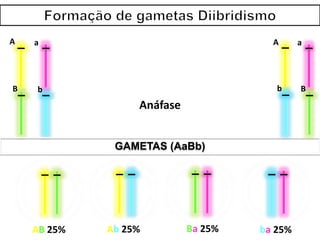
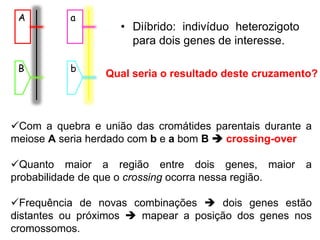
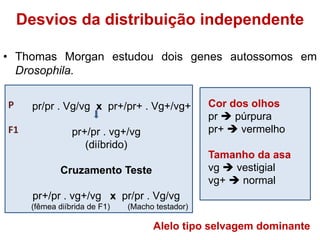
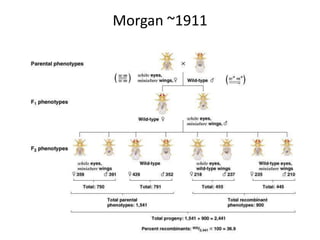
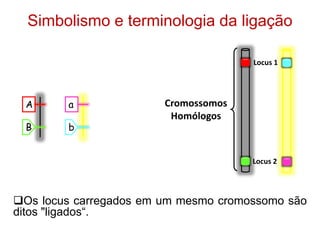
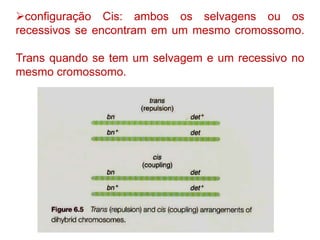
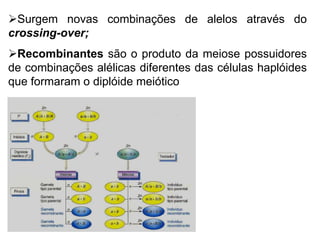
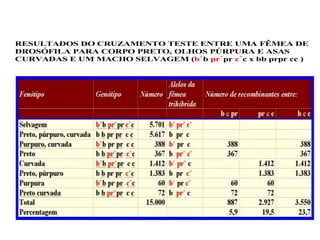
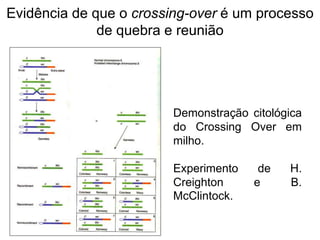
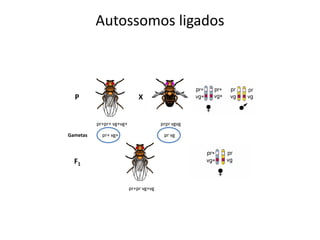
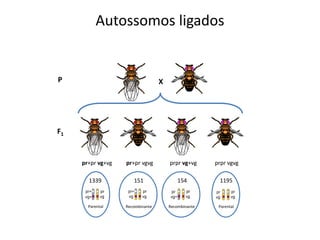
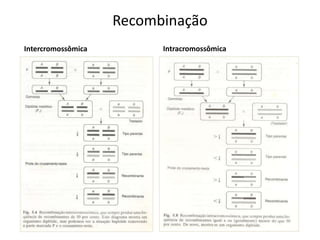
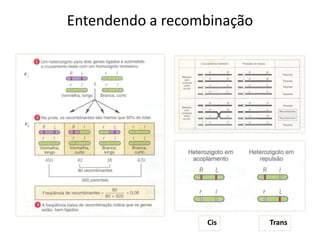
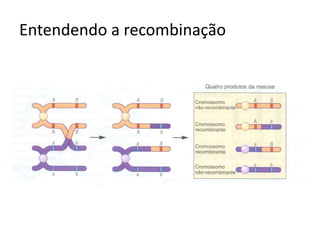
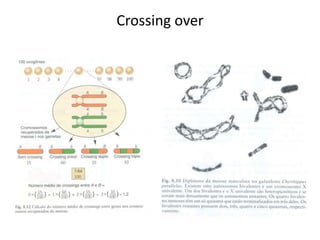
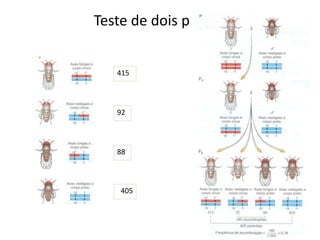
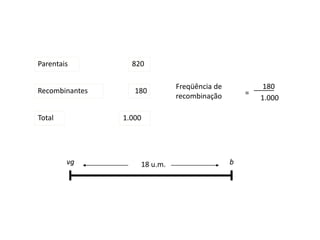
O documento discute a recombinação genética durante a meiose. A recombinação ocorre quando segmentos de DNA são trocados entre cromossomos homólogos, resultando em novas combinações de alelos e aumentando a diversidade genética. O processo envolve a quebra e religação do DNA, formando junções de Holliday que podem ser resolvidas de forma a gerar cromossomos recombinantes ou não. A taxa de recombinação entre loci é usada para mapear a posição relativa dos genes nos cromossomos.