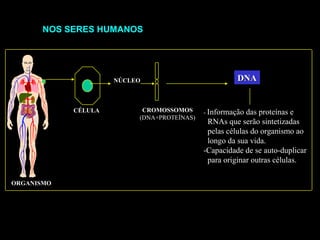
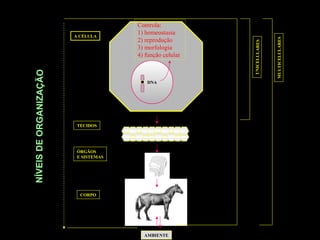
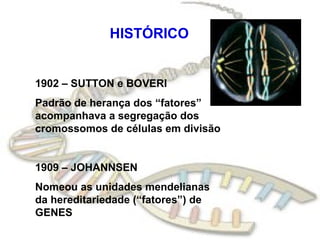
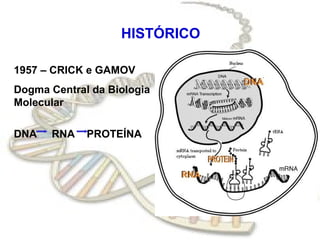
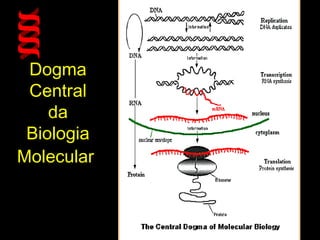
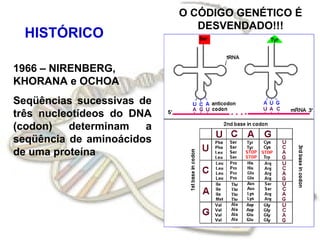
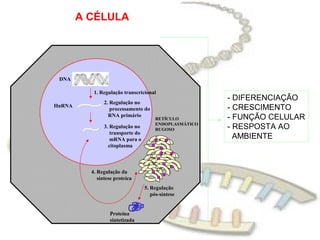
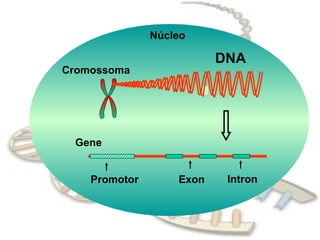
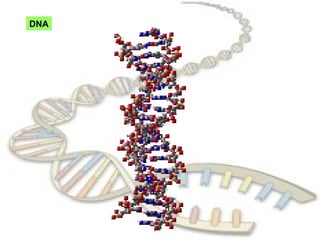
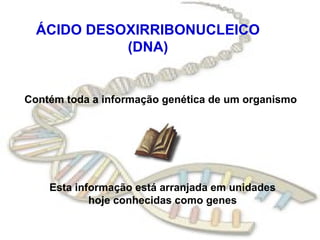
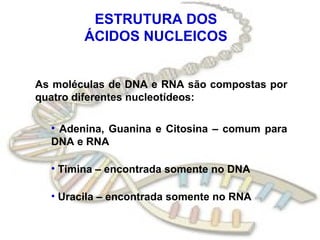
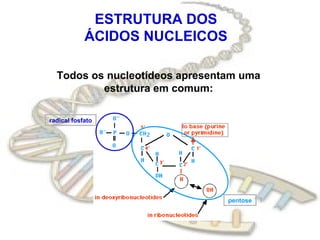
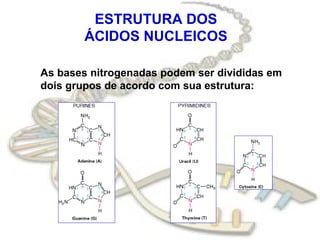
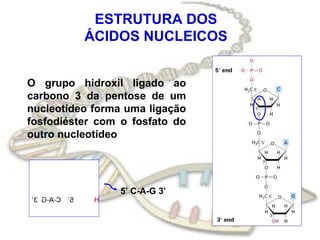
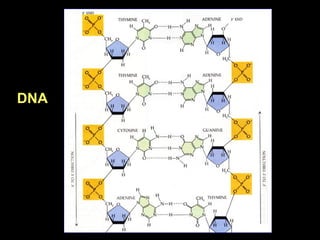
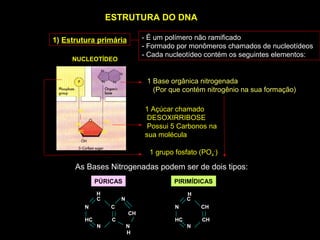
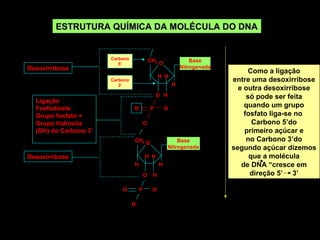
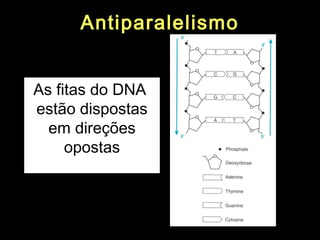
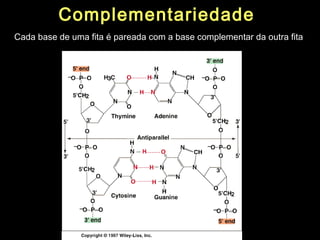
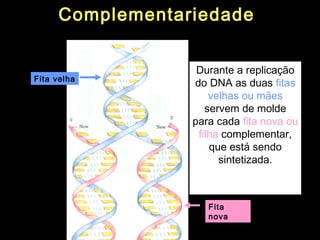
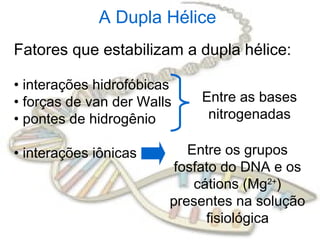
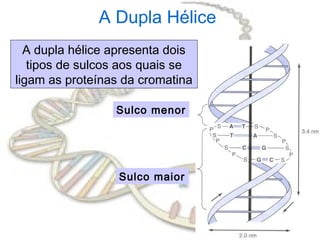
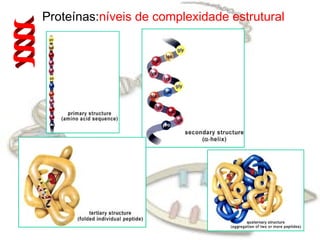
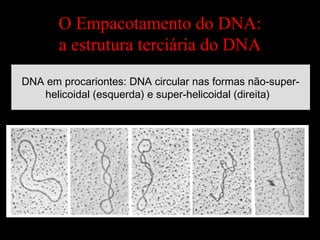
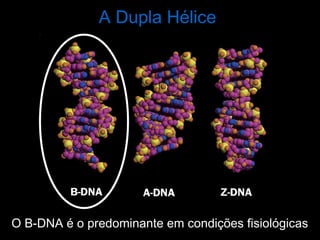
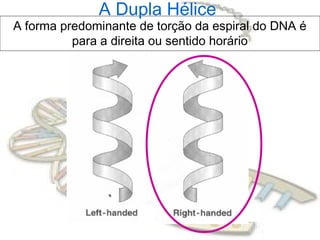
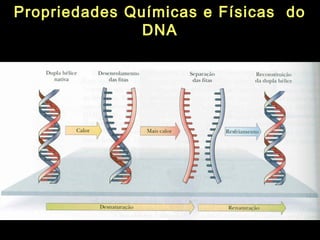
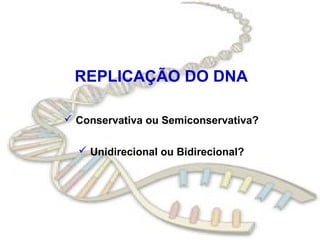
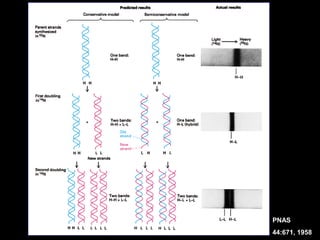
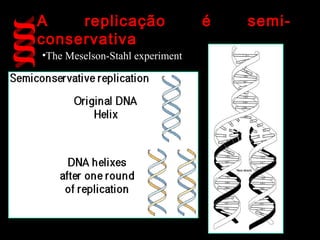
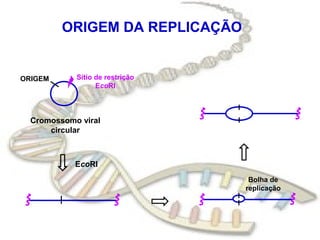
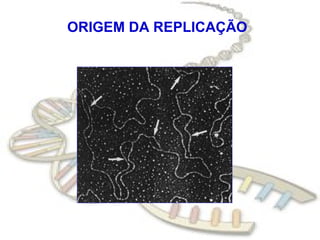
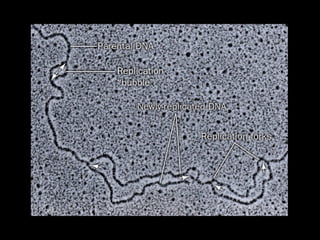
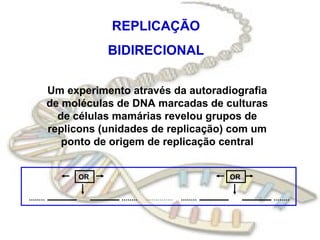
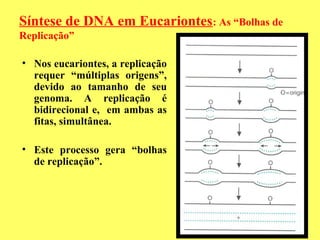
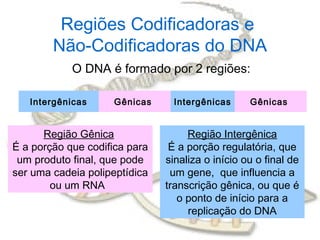
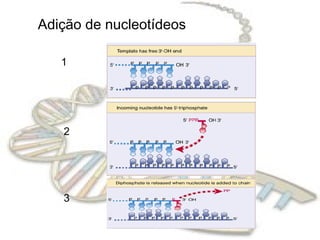
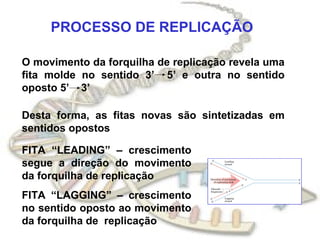
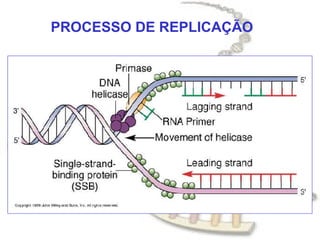
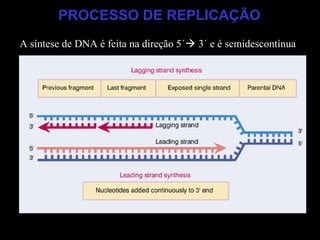
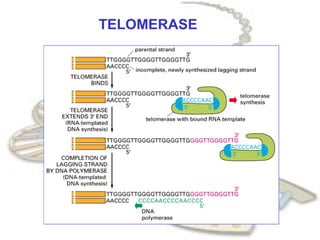
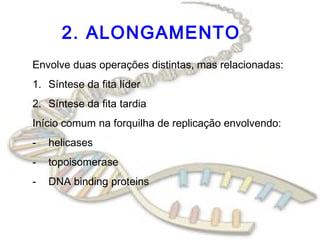
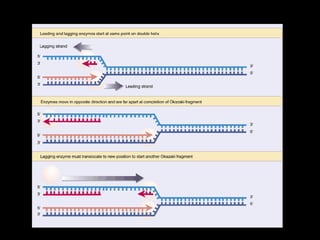
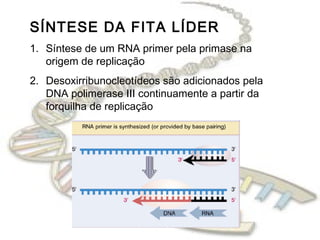
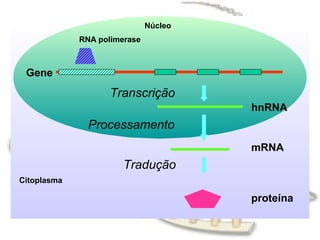
O documento fornece uma introdução à biologia molecular, descrevendo: 1) A estrutura do DNA e como ele armazena e transmite informações genéticas; 2) Os principais eventos históricos que levaram à compreensão da estrutura do DNA e de como ele controla as células e organismos; 3) Os processos de replicação do DNA, transcrição e tradução que permitem a expressão dos genes.